Il progetto
ESCOGITARE è il progetto in cui noze ha collaborato con l’ISTI — Istituto di Scienza e Tecnologie dell’Informazione “A. Faedo” del CNR di Pisa — per la realizzazione di un sistema di creazione e condivisione di esperimenti bioinformatici rivolto a una comunità di biologi distribuita su tutta Italia.
Lo scopo del sistema è dare a ricercatori e laboratori uno strumento web in cui:
- comporre workflow scientifici in modalità visuale (senza scrivere codice)
- eseguirli su una griglia computazionale già esistente
- condividere sia i workflow che i risultati con il resto della comunità scientifica
- pubblicare informazioni su progetti, esperimenti, banche dati, news e materiali correlati
I risultati sono stati presentati al convegno conclusivo del 5 febbraio 2010 a Pisa presso ISTI-CNR.
Il consorzio
- ISTI-CNR Pisa — Istituto di Scienza e Tecnologie dell’Informazione “A. Faedo”
- CRA — Consiglio per la Ricerca e la sperimentazione in Agricoltura, con i suoi due istituti coinvolti nel progetto:
- ISSDS-CRA Firenze — Istituto Sperimentale per lo Studio e la Difesa del Suolo
- ISC-CRA Fiorenzuola — Istituto Sperimentale per la Cerealicoltura
- Research Center on Software Technology
- noze — sviluppo del portale, dell’interfaccia visuale e dell’integrazione con la griglia
A seguito della riforma del 2015 il CRA e i suoi istituti sono confluiti nel CREA — Consiglio per la ricerca in agricoltura e l’analisi dell’economia agraria, che oggi porta avanti la missione di ricerca dei partner agricoli del progetto.
Il ruolo di noze
noze si è occupata di tre cose principali, lungo tutto lo stack:
1. Interfacciamento al grid esistente
ISTI-CNR aveva già un grid computazionale funzionante (basato su Globus Toolkit, Active BPEL e MDS). noze lo ha interfacciato con un sistema di gestione dei workflow scientifici, in modo che le operazioni di amministrazione, deploy e run degli esperimenti diventassero accessibili dal portale web — senza richiedere agli utenti competenze sysadmin sul grid. Tra le funzioni di amministrazione esposte: shutdown container Globus, deploy/undeploy GAR, query indice servizi, rimozione macchine, stop IP-forwarding.
2. Visual Workflow Designer
Il componente più caratteristico realizzato da noze: un editor visuale drag&drop per la composizione di workflow scientifici condivisibili tra ricercatori. La palette dinamica contiene macroblocchi specializzati per la bioinformatica (FBClustalW, FBCondition, FBHuman, FBMPIBlast, FBPrimer3, FBReceiveSequence, FBSequence2Primer3Adapter), riutilizzabili e configurabili. I workflow disegnati visualmente vengono tradotti automaticamente in BPEL ed eseguiti dall’Active BPEL Engine sulla griglia Globus.
L’obiettivo di design: mantenere l’editor il più semplice possibile, per consentire l’uso anche a un pubblico tipicamente non informatico (biologi e ricercatori di laboratorio), senza dover scrivere codice o BPEL a mano.
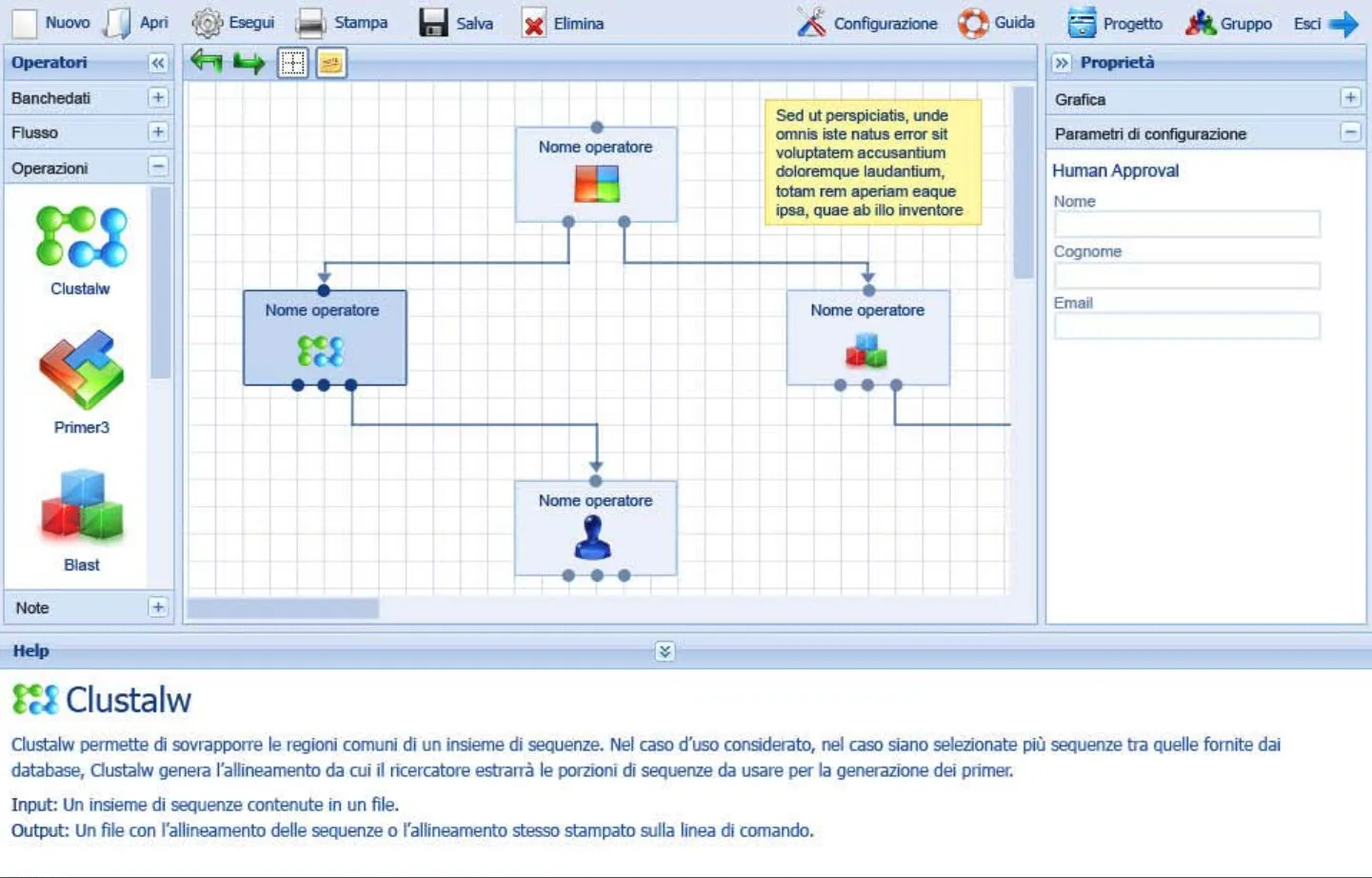
Screenshot del Visual Workflow Designer: a sinistra la palette degli operatori (ClustalW, Primer3, Blast), al centro il canvas con i blocchi connessi che compongono un workflow bioinformatico, a destra il pannello dei parametri di configurazione, in basso l’help contestuale.
3. CMS e portale web 2.0
noze ha integrato l’intero sistema di gestione dei workflow con un CMS che si occupa della pubblicazione dei contenuti relativi ai progetti e agli esperimenti bioinformatici (sezioni Progetti, Ricerca, Banche dati, Forum, AccessGrid, News & Events).
Lo stile del CMS è stato disegnato per integrarsi visivamente con le altre parti del portale — il Visual Workflow Designer, l’interfaccia di amministrazione della griglia e l’interfaccia di gestione dei progetti e dei workflow — in modo che l’utente percepisca un unico ambiente coerente, non l’aggregazione di tool separati.
Approccio Web 2.0 e usabilità
La progettazione grafica del portale segue i principi del Web 2.0 — un approccio a internet che integra aspetti grafici, funzionali e collaborativi — perché lo scopo del sistema è esattamente quello di abilitare una grande comunità di biologi alla composizione e condivisione di workflow scientifici.
Oltre alla griglia di calcolo, il portale supporta anche AccessGrid per la videoconferenza scientifica multi-sito, completando l’esperienza di collaborazione distribuita.
Caso d’uso bioinformatico
Un esperimento “in silico” tipico implementato nella piattaforma:
- Ricerca di sequenze tramite collegamento a GeneBank
- Allineamento di più sequenze tramite ClustalW
- Design dei primer più appropriati tramite Primer3
- Verifica di specificità delle sequenze tramite BLAST
- Test e verifiche in laboratorio sui risultati
L’intero workflow viene composto visualmente nell’editor di noze, eseguito sulla grid Globus tramite BPEL, e condiviso con la comunità attraverso il portale.